Vous êtes ici
Les nouveaux territoires du vivant
Cet article est paru dans le premier numéro de la revue Carnets de Science.
Faisons un pari : le XXIe siècle sera celui des sciences du vivant. Pourquoi cette prédiction ? Tout simplement parce que la biologie vit en ce moment une véritable révolution. Et même plusieurs révolutions en même temps, provoquées par des progrès technologiques phénoménaux grâce auxquels on peut désormais observer des organismes vivants jusqu’à l’intérieur de leurs cellules, analyser et manipuler leur ADN en toute facilité et croiser les milliards d’informations du big data. C’est une nouvelle ère qui s’ouvre, dans laquelle les scientifiques espèrent (rien de moins) comprendre enfin les origines de la vie, explorer les ramifications insoupçonnées de l’arbre du vivant, reconstituer l’histoire biologique de l’humanité, décrypter la logique complexe du fonctionnement des êtres vivants, percer les mystères du cerveau…
Avec un héritage de plus de deux mille ans de recherches, le XXIe siècle aurait pu s’inscrire dans l’assurance que nous, les biologistes, étions désormais dotés à la fois d’une vision globale du vivant et de son histoire évolutive, mais aussi de la capacité à percer les secrets de son fonctionnement intime. C’est tout le contraire : aujourd’hui, nous avons pris conscience que nous méconnaissons l’étendue de la biodiversité, que l’histoire de la vie, les mécanismes de l’hérédité des caractères et le fonctionnement du vivant ne sont pas guidés par les seuls lois et dogmes que nous avons établis jusque-là. Ce qui revient à dire que l’exploration du vivant, de son histoire et de son fonctionnement est devant nous.
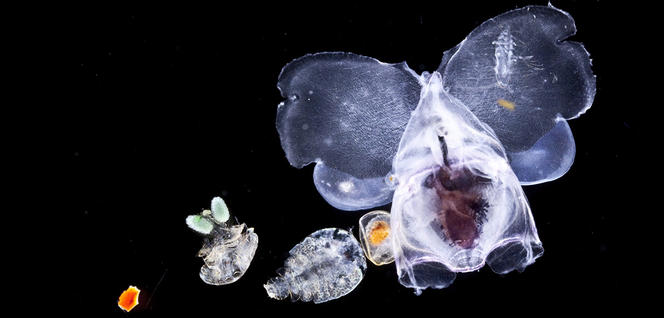
De la vie partout, jusque dans les puits de pétrole
Comment expliquer cette remise en question ? La réponse réside probablement dans cette phrase de Sydney Brenner (prix Nobel de physiologie ou médecine, 2002) : « L’avancée de la science découle de nouvelles techniques, de découvertes et de nouvelles idées, probablement dans cet ordre. » Les sciences de la vie ont déjà connu des avancées majeures dues au développement de nouveaux outils technologiques, comme l’invention du microscope. Mais rien d’une ampleur comparable avec la puissance des nouvelles techniques développées depuis une vingtaine d’années, de la métagénomique à la technologie CRISPR-Cas9.
Alors quels sont les grands champs inexplorés qui s’ouvrent à nous ? Le premier qui s’est amorcé est la découverte d’êtres vivants dans des milieux particulièrement inhospitaliers, que l’on pensait incompatibles avec la vie. C’est ainsi que les geysers, les fumeurs noirs ou les puits de pétrole, caractérisés par des températures qui dépassent 100 °C, sont peuplés de micro-organismes. Mais la vie est aussi abondante dans les mers glacées des pôles, au sein du Grand Lac salé de l’Utah, de la mer Morte (finalement mal nommée), des marais salants qui sont « habités » en dépit de taux de sel ou de soufre toxiques. Entre Éthiopie et Érythrée, à Dallol, l’un des endroits réunissant les conditions les plus extrêmes sur Terre, des eaux bouillonnantes et hyperacides viennent de révéler des micro-organismes encore jamais identifiés.
Les surprises jaillissent aussi de la découverte d’organismes qui ne trouvent pas leur place dans la classification actuelle du vivant. C’est le cas de ce qu’on appelle les mégavirus ou virus géants. Géants par leur taille et par leur génome, et totalement surprenants par différents caractères qui les distinguent des virus sans les faire pour autant entrer dans la catégorie du vivant. Il a fallu attendre 2003 pour découvrir ces monstres qui sont pourtant omniprésents dans la nature. Comment fonctionnent-ils ? Sont-ils les rejetons de cellules primitives ? Forment-ils la quatrième branche du vivant ?
Enfin, il y a la prise de conscience de l’immensité de la biodiversité. À bord du navire Beagle, Charles Darwin avait étudié nombre d’espèces marines et terrestres de grandes tailles et de cette étude avait émergé la théorie de l’évolution. À bord de Tara, les chercheurs se sont penchés sur les micro-organismes planctoniques marins (virus, bactéries, êtres unicellulaires et micro-animaux) et leur étude bouleverse déjà l’état de nos connaissances sur cette population d’organismes dérivants. Plus de 60 % des bactéries de la planète vivent dans les océans, mais nous en connaissons… moins de 5 % !

L’intestin : un charme discret mais un rôle vital
Autre continent microbien que l’on commence à explorer : celui des microbiotes, populations soudées de bactéries, champignons et virus, qui se logent au sein d’un organisme vivant. Si chaque litre d’eau de mer contient 10 à 100 milliards de micro-organismes, c’est pire dans l’intestin : 100 000 milliards de bactéries tapissent nos 400 m2 de surface intestinale, soit une masse de 1 à 5 kilos et un nombre de cellules et de gènes cent fois plus important que celui de notre propre organisme. C’est le microbiote intestinal, un ensemble de communautés au taux de renouvellement très rapide et aux interactions intenses, une ressource énorme de formes de vie et de composés bioactifs inexplorés. 85 % de ces espèces révélées par la métagénomique nous sont inconnues, car impossibles à cultiver et donc à étudier en laboratoire pour le moment. C’est pourtant là un défi à relever tant les fonctions du microbiote se révèlent peu à peu essentielles : au-delà de son action dans la digestion des aliments, il permet la maturation de notre système immunitaire et nous protège contre des bactéries étrangères, contrôle notre croissance et module le fonctionnement de notre système nerveux, intervenant dans nos comportements, tant alimentaires que psychiques : il interviendrait même dans des troubles neuropsychiatriques, comme l’autisme, la dépression et la schizophrénie… Il faut donc le considérer comme l’un de nos organes, faisant de notre organisme une machine hybride homme-microbes.
Ce monde inconnu qui commence à peine à être dévoilé ne remet pas en question les propriétés qui fondent la vie : auto-organiser des complexes macromoléculaires et maintenir la mémoire de cette organisation alors même que les constituants sont en permanence remplacés, mobiliser l’énergie nécessaire pour la constitution de cette matière et son organisation (un « métabolisme ») et se reproduire plus ou moins à l’identique. Son unité reste la cellule, douée des trois propriétés précédentes, et délimitée par une membrane. Les ingrédients de la vie sont également toujours les mêmes : acides nucléiques, protéines, lipides et glucides.
Alors où est le tournant ? Il se situe dans la découverte de l’immense biodiversité des formes microbiennes inconnues et de la formidable ingéniosité dont celles-ci font preuve pour coloniser des milieux que l’on pensait impropres à la vie. Grâce à ces découvertes, notamment dans des milieux qui pourraient être similaires à ceux qui ont précédé la vie il y a plus de trois milliards d’années sur notre planète, la question de l’origine de la vie va sortir de l’ère des récits improbables pour aborder une phase d’expérimentation capable de livrer des scénarios probables.
Comprendre comment les espèces évoluent (ensemble)...
Les mécanismes à la base de l’évolution sont également chahutés. Longtemps centrés sur la prééminence de la mutation aléatoire des gènes, on découvre aujourd’hui d’autres moteurs puissants à l’origine de l’innovation biologique et de l’évolution. Citons par exemple l’importance des transferts de gènes d’une espèce à l’autre, comme l’illustrent les syncytines, deux protéines nécessaires à la formation du placenta des mammifères. Surprise : leurs gènes ont été légués par des rétrovirus ! L’apparition des mammifères placentaires il y a près de cent millions d’années pourrait ainsi être liée à la capture d’un rétrovirus qui aurait permis de passer d’un mode de développement embryonnaire « externe » (chez les animaux qui pondent des œufs) au mode « interne » des mammifères chez lesquels l’embryon est alimenté via le placenta. Citons encore l’endosymbiose, une collaboration bénéfique entre deux organismes vivants dont l’un est contenu par l’autre. Avec le temps, l’organisme « contenu » peut aller jusqu’à perdre totalement son autonomie pour devenir une partie de celui qui le contient. Cela est illustré par l’origine bactérienne des mitochondries.
Le temps de l’évolution est également remis en question. Après avoir considéré depuis Darwin qu’il était lent (des millions d’années), nous savons désormais qu’il peut se limiter à quelques années : c’est en moins de cinquante ans que l’on a vu les adaptations ou échecs d’adaptation de la mésange bleue en Corse et dans la zone montpelliéraine. On peut donc observer l’évolution en action en milieu naturel, mais aussi faire de l’évolution expérimentale en laboratoire ! C’est le cas de la célèbre expérience de Richard Lenski publiée en 2013. Pendant vingt-cinq ans, le chercheur a étudié des milliers de générations de bactéries issues d’une même souche et a pu décrypter plusieurs mécanismes à la source de l’évolution…
Les nouvelles technologies ouvrent aussi l’accès à l’évolution de temps très anciens. Les analyses des ADN fossiles permettent de mesurer les variations génétiques d’une lignée sur quelques centaines de millions d’années. C’est ainsi qu’on découvre de nouvelles lignées humaines dont on ne pouvait pas soupçonner l’existence. Citons l’énigmatique homme de Denisova, qui a cohabité avec l’homme de Neandertal et Homo sapiens, trois lignées ayant eu à plusieurs reprises des rapports sexuels féconds. Ce qui explique la présence d’ADN « néandertalien » et « dénisovien » dans notre génome et met en lumière l’importance des brassages génétiques dus à ces métissages dans les succès évolutifs. Ces découvertes renvoient aux grands mécanismes présidant à l’apparition et à l’extinction des espèces, des phénomènes continus mais qui ont traversé des crises, comme celle sans précédent dont nous sommes actuellement les témoins, les victimes et les acteurs.



À l’assaut de la complexité du vivant
Les organismes vivants sont caractérisés par une extrême complexité. Complexes car issus de l’assemblage de milliards de macromolécules et cellules, car dynamiques et en constant renouvellement, car étonnamment cohérents dans la coordination de leurs différentes parties, car capables de s’auto-organiser en obéissant à une mémoire intrinsèque, car soumis à une variabilité individuelle tout en gardant la mémoire de plans d’organisation généraux… Cette complexité a longtemps été abordée en faisant des analyses à différentes échelles (gène, protéine, cellule) et en tentant ensuite de les relier. Mais faire ainsi la somme de ses parties n’a pas livré la vision de l’ensemble. Plus : l’analyse de chaque partie l’a révélée à nouveau comme un monde en elle-même, dont les chercheurs avaient sous-estimé la complexité.
En ce début de siècle, quelles sont les percées ? Commençons par les bouleversements que traverse la biologie de la cellule, grâce notamment à la possibilité nouvelle d’accéder au génome et aux produits de son expression, ARN et protéines, d’une seule cellule. Évoquons les cellules souches. En 2007, l’équipe de Shinya Yamanaka (prix Nobel de physiologie ou médecine, 2012) a ainsi révélé qu’il suffit d’exprimer quatre protéines dans une cellule adulte pour la reprogrammer vers un retour à son origine, la cellule souche. Ce que nous disent les travaux récents, c’est que rien n’est finalement irréversible dans les destins cellulaires : la plasticité est au cœur du vivant, garante d’une robustesse exceptionnelle de son fonctionnement.
Autre bouleversement pour les scientifiques : la prise en compte des forces mécaniques mises en jeu dans l’organisation et le fonctionnement de la cellule. C’est ainsi que la compréhension des divisions ou des migrations cellulaires passe par la connaissance de la façon dont les forces sont générées et dont elles produisent des déformations. Cela est abordé de nos jours par des approches totalement novatrices, basées entre autres sur des techniques à l’échelle nanométrique qui permettent de contrôler et de moduler les paramètres physico-chimiques de la cellule et de son environnement.
La séquence de l’ADN n’explique pas tout
La biologie moléculaire avait consacré l’ADN comme LA molécule support de l’hérédité. Le décryptage de sa séquence devait livrer la connaissance des fonctions biologiques et des comportements les plus complexes et intimes des organismes vivants et permettre de prédire ceux de leurs descendants. Mais de nombreuses découvertes récentes sont venues compliquer ce scénario. À commencer par celle d’une organisation extrêmement élaborée qui permet de condenser les 2 mètres d’ADN du génome humain dans un noyau cellulaire d’un diamètre de 5 à 10 microns. Au-delà de la condensation, ces reploiements de l’ADN délimitent des zones actives où les gènes peuvent s’exprimer et des zones inactives où ils ne s’expriment pas. Cette combinaison de régions actives et silencieuses est propre à chaque type de cellule, expliquant que chez un même individu, alors qu’elles sont pourtant dotées d’un génome identique, les cellules sont dotées de caractéristiques et fonctions bien spécifiques : impossible de confondre une cellule musculaire avec une cellule hépatique ou un neurone…
Mieux, ces cellules maintiennent ces combinaisons de zones de façon stable et les transmettent lors de leur division à leurs cellules filles, une propriété essentielle mais incomprise à l’heure actuelle. Toujours plus surprenant, cette transmission peut s’étendre dans certains cas aux générations suivantes. La transmission de telle ou telle disposition de l’ADN confère des caractères distincts à la descendance alors que la séquence de cet ADN est identique. Nous sommes dans le domaine de l’hérédité épigénétique, avérée chez beaucoup d’organismes unicellulaires, chez les plantes et chez certains animaux, mais a priori très limitée chez les vertébrés, dans la mesure où leur génome est réorganisé de novo lors de la formation des gamètes. Néanmoins, ces mécanismes sont à l’œuvre dans toutes nos cellules. D’où cette question cruciale : quelles sont les parts génétique, épigénétique et environnementale dans le fonctionnement des organismes vivants et dans l’hérédité ?
Dans ce grand tournant qui a signé la fin du rêve du tout-génomique, un autre dogme s’est effondré : celui selon lequel l’ARN ne constituerait qu’un intermédiaire entre le stockage de l’information génétique par l’ADN et l’exécution des fonctions cellulaires par les protéines. Dans le déluge de données livrées par les nouvelles technologies apparaît le monde des ARN dits non codants, ainsi appelés parce qu’ils ne sont pas destinés à être traduits en protéines. Ils sont issus de l’expression des immenses zones du génome longtemps qualifiées d’ADN « poubelle »… Grave erreur. Depuis le début de ce siècle, les chercheurs se penchent sur les fonctions de ces ARN et leur découvrent des rôles essentiels dans la régulation épigénétique, dans le contrôle de l’expression des gènes, le trafic des molécules à l’intérieur des cellules ou les communications entre cellules.
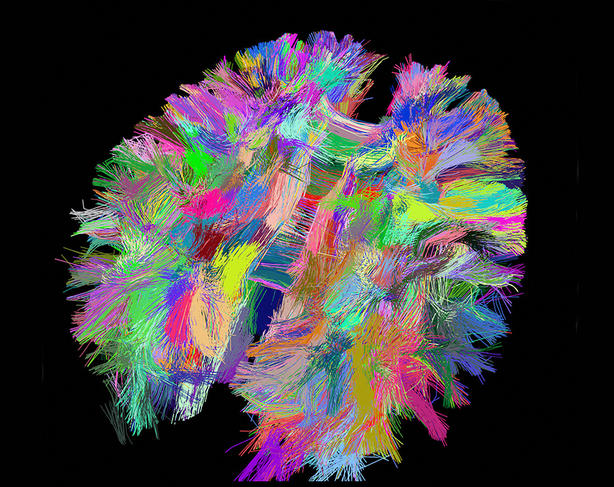
Le cerveau, Graal des biologistes
Terminons ce tour incomplet des promesses de la biologie du XXIe siècle par l’une des questions qui fascine le plus l’humanité : celle du propre de l’être humain, la conscience de soi, qui lui permet d’appréhender sa propre existence et, derrière cela, ce qui permet son émergence, le cerveau humain. Il s’agit d’une part de comprendre comment fonctionne cet organe mais aussi, et ce qui est beaucoup plus compliqué, de cerner la manière dont la conscience émerge de ce fonctionnement : comment les assemblages de neurones peuvent-ils conduire à des expériences mentales ? Quel est le code neural, inconnu aujourd’hui, qui permet à la biologie moléculaire et cellulaire du cerveau de générer des fonctions très spécifiques non seulement au cerveau humain (mémoire, reconnaissance des objets…) mais aussi à l’être humain dans sa dimension sociale (conscience du corps et de soi, pensée, langage, symboles, relations avec autrui…) ? Les avancées spectaculaires de cette science reposent sur les technologies en plein essor d’imagerie cérébrale humaine. Celles-ci permettent de mesurer et de visualiser les états d’activité des structures cérébrales et de connecter comportement et activité cérébrale. C’est ainsi qu’a commencé le décryptage des bases cérébrales de l’arithmétique et de la numération, de la lecture et du langage, de la mémoire et de l’apprentissage, de la conscience et de la pensée…
Les progrès et les changements profonds que vivent les sciences du vivant en ce début de siècle révèlent les transformations qu’elles sont susceptibles de provoquer dans l’évolution de nos sociétés et dans celle de la planète. Bien que son cerveau soit doté de fonctions supérieures qui le distinguent des autres animaux, l’homme n’en demeure pas moins un maillon de la chaîne évolutive et n’en est pas son aboutissement. Décrypter les mécanismes biologiques du vivant dans son ensemble contribue donc à mieux comprendre le fonctionnement du corps humain et ses dérèglements pathologiques. Gardons en mémoire que c’est une recherche libre à tous les étages qui a produit beaucoup des outils diagnostiques et thérapeutiques d’aujourd’hui et que c’est à cette condition qu’elle gardera la capacité d’en produire encore pour demain. Et qu’au-delà de leurs applications, les savoirs qui sont issus de ces recherches sont un bien culturel essentiel aux sociétés et une formidable arme de lutte contre l’obscurantisme.
À lire :
Étonnant vivant. Découvertes et promesses du XXe siècle, Catherine Jessus (dir.), CNRS Éditions, 30 mars 2017, 328 p., 20 €
À lire / À voir
Étonnant vivant. Découvertes et promesses du XXe siècle, Catherine Jessus (dir.), CNRS Éditions, mars 2017, 328 p., 20 €